Contribuições do estudo
Principais resultados
O principal resultado deste trabalho é o modelo metodológico padronizado de vinculação de dados de diferentes sistemas de informações em saúde pública.
INTRODUÇÃO
A vigilância em saúde é definida como um processo contínuo e sistemático de coleta, consolidação, análise de dados e disseminação de informações sobre eventos relacionados à saúde, com vistas ao planejamento e implementação de medidas de saúde pública que incluem a regulação, intervenção e atuação em condicionantes e determinantes da saúde, para proteção e promoção da saúde da população, prevenção e controle de riscos, agravos e doenças.1
A integração dos sistemas de informações em saúde (SIS) é uma importante estratégia descrita na Política Nacional de Vigilância em Saúde (PNVS), no sentido de contribuir com o aprimoramento e consolidação da gestão da vigilância em saúde, especialmente nas atividades de planejamento, monitoramento e avaliação das ações de vigilância, em tempo oportuno.1 Os SIS são ferramentas tecnológicas que auxiliam o processamento de dados coletados em serviços de saúde e outros locais, gerando informações úteis para a compreensão dos problemas e subsídio à tomada de decisão no âmbito das políticas e do cuidado em saúde.2,3
No Brasil, o Ministério da Saúde é responsável pela gestão dos SIS de base nacional. Entre os diversos SIS, os mais utilizados são: o Sistema de Informações sobre Mortalidade (SIM), o Sistema de Informações sobre Nascidos Vivos (Sinasc), o Sistema de Informação de Agravos de Notificação (Sinan), o Sistema de Informações Hospitalares do Sistema Único de Saúde (SIH/SUS), o Sistema de Informação de Vigilância Epidemiológica (Sivep) e, recentemente, o sistema e-SUS Notifica. Apesar da disponibilidade e aperfeiçoamento de diversos SIS nas últimas décadas, a interoperabilidade entre eles ainda não ocorre nos setores da vigilância em saúde.2
Frente à necessidade de se trabalhar com informações qualificadas, que mantenham integração entre os diferentes SIS, o relacionamento de base de dados apresenta-se como uma estratégia viável, com o propósito de materializar essa conexão de diferentes informações.4 A técnica de linkage, de relativo baixo custo operacional, permite a recuperação de registros incompletos ou inconsistentes e, com isso, melhora a completitude e a confiabilidade das informações disponibilizadas pelos SIS.5
Embora estudos anteriores evidenciem as vantagens do emprego de linkage para a análise da qualidade de diversos SIS,6-9 há uma escassez de estudos metodológicos que apresentem os procedimentos necessários à realização dessa técnica. Assim, este manuscrito justifica-se pela importância de disseminar metodologias utilizadas na vigilância em saúde, na padronização metodológica de vinculação de dados e no fornecimento de modelos de análise possíveis de serem adaptados a diferentes realidades e áreas de conhecimento da saúde.
O objetivo deste trabalho foi apresentar um método padronizado para a vinculação de diferentes bancos de dados em saúde pública.
MÉTODOS
Artigo de revisão metodológica, sobre vinculação de bancos de dados de diferentes sistemas de informações, considerando procedimentos técnicos realizados no âmbito da vigilância em saúde do Ministério da Saúde. Este material foi desenvolvido para utilização no software R, a partir de bancos de dados simulados com informações hipotéticas sobre nome do paciente, nome da mãe e sua data de nascimento.
Os métodos descritos a seguir são replicáveis para quaisquer dados de diferentes SIS, e estes são focados no processo de vinculação determinística, que realiza a classificação dos possíveis pares com base em regras de combinação que prezam pelo pareamento de registros idênticos.10
Preparação dos bancos de dados
É importante que, antes de iniciar o processo de vinculação de dados, sejam definidas as variáveis a serem utilizadas para a análise dos dados vinculados. Essa definição subsidiará o processo de tratamento dos dados, pois, ao se trabalhar com bancos de dados de grande magnitude, pode ser necessário diminuir o tamanho do banco para que a máquina (computador) processe os dados com maior facilidade, evitando-se problemas de performance. Além disso, o software R pode apresentar mau funcionamento, por limitação de memória interna do programa ao se utilizar em bancos de dados de grande magnitude. Assim, é recomendável trabalhar com objetividade, utilizando-se apenas as variáveis de interesse, para melhor eficiência do processo de vinculação.
Software R para vinculação
Sugere-se a utilização do software R no processo de desenvolvimento do roteiro de tratamento e vinculação de dados.
Será necessário realizar a instalação dos pacotes lubridate11 (que permite o tratamento de variáveis do tipo “data”, como, por exemplo, “Data de notificação”), abjutils12 (permite a remoção de acentos gráficos) e tidyverse;13 para simular dados nominais, sugere-se o pacote e função “randomNames”.14
O pacote tidyverse13 engloba outros pacotes, mais frequentemente utilizados no tratamento e análise de dados, como: ggplot2 (permite a produção de gráficos), dplyr (manipulação de dados), tidyr (organização dos dados), readr (leitura de arquivos .csv), purrr (permite trabalhar com funções e vetores), tibble (leitura de bancos de dados em formato de texto .txt), stringr (permite trabalhar com variáveis nominais) e forcats (tratamento de variáveis categóricas) - comando: install.packages(“tidyverse”). Caso o software seja fechado, deve-se utilizar a função library para carregamento dos pacotes de interesse, já instalados - comando: library(tidyverse).
Tratamento de dados
É importante que as etapas descritas a seguir sejam replicadas seguindo a mesma ordem de instruções deste passo a passo, para evitar erros.
Inicialmente, deve-se definir o diretório de trabalho (pasta de arquivos) com a função setwd. Nesse diretório, devem ser inseridos os bancos de dados que serão vinculados - comando: setwd(“C:/Users/User/Desktop/Pasta de trabalho”).
Para importação dos bancos de dados ao ambiente do R, sugere-se a utilização da função read.csv2 - que importa arquivos do tipo csv com separador de “;” ao invés de “,”. Para bancos de dados no formato de texto (txt), deve-se utilizar a função read.table e definir a primeira linha como um cabeçalho de variáveis, o separador de células para “;” e o marcador decimal para “,”. Caso sejam utilizados arquivos do tipo xls ou xlsx, deve-se utilizar o comando readxl::read_excel(“arquivo.xlsx”). Para arquivos do tipo dbf ou dbc,15 comuns para dados do Sinan, é necessária a instalação dos pacotes “foreign”16 e “read.dbc”,17 e utilização dos comandos read.dbf(“arquivo.dbf”) e read.dbc::read.dbc(“arquivo.dbc”) respectivamente.
Sugere-se a atribuição do primeiro banco de dados importado a um objeto de armazenamento do R, denominado “Banco_1”, e o segundo banco a outro objeto, denominado “Banco_2” - comando: Banco_1 <- read.csv2(“Banco de dados 1.csv”); ou read.table(“Banco_1.txt”, header = TRUE, sep = “;”, dec = “,”).
Para cada banco de dados, sugere-se a exclusão das variáveis que não serão utilizadas, por meio do comando “Banco_1$variavel <- NULL”. Quando a quantidade de variáveis a serem retiradas for grande, sugere-se, ao invés da exclusão, a seleção das variáveis de interesse, por meio da função select e atribuição desse novo conjunto ao mesmo objeto anteriormente criado - exemplo: Banco_1 <- select(Banco_1, variavel1, variavel3, variavel5).
É essencial que sejam mantidas as variáveis que serão utilizadas como chaves para a vinculação, junto às que serão analisadas. Sugere-se a utilização das variáveis referentes ao nome da pessoa notificada, CPF e data de nascimento, e o nome da mãe, por serem as chaves mais frequentemente utilizadas na literatura científica. Apesar de incomum em bancos de dados dos SIS, a utilização da variável “CPF” pode ser entendida como uma variável que possui pontos e hífen em sua estrutura. Esta situação configura o CPF como uma variável do tipo character, e, para sua utilização como uma variável numérica (numeric ou integer), é necessário limpar esses pontos e hifens das observações. Além disso, o preenchimento do CPF pode ser feito de diferentes formas, nas notificações desses SIS, contendo ou não hifens e pontos. Devido a essa falta de padronização no preenchimento de variáveis desse tipo, sugere-se a remoção desses sinais para o melhor aproveitamento dessas chaves.18-20
Para a padronização das variáveis “nome” e “CPF”, sugere-se que estas sejam do tipo character (texto). Quando for necessária a conversão dessas variáveis, deve-se utilizar o comando as.character(Banco_1$variável_1). Para o CPF, deve-se retirar os pontos “.” e traços “-” (comando: Banco_1$CPF <- str_replace_all(Banco_1$CPF, “\\.|-”, “”), e adicionar dígitos zero “0” à esquerda do texto até completar 11 dígitos (comando: Banco_1$CPF <- str_pad(RAIS Banco_1$CPF, 11, pad=”0” ).
Para a variável “data do nascimento”, é preciso conferir se seu formato aparece como “Date” (data) no ambiente R. A checagem do tipo da variável pode ser feita com a função class - comando: class(Banco_1$Data_nascimento).
Datas, no R, são exibidas da seguinte forma: 2020-12-31 (ano-mês-dia). Caso a variável não esteja no formato “Date”, cumpre convertê-la para este formato por meio de funções do pacote lubridate,11 por exemplo, via comando: Banco_1$Data_nascimento <- as.Date(Banco_1$Data_nascimento). Outras variáveis deste comando podem ser utilizadas, como dmy (para datas escritas em dia-mês-ano) ou ymd (para datas em ano-mês-dia).
Para as variáveis de “Nome”, deve-se, nesta ordem, substituir as letras acentuadas por letras sem acentuação gráfica - por exemplo; substituir “Á” por “A”, “Õ” por “O” e demais opções. Podem-se também retirar conectores de sobrenomes, como “E”, “A”, “DA”, “DE”, “DO”, “DAS”, “DES” e “DOS” - por exemplo; “MARIA DOS ANJOS” torna-se “MARIA ANJOS”. Sugere-se a transformação das letras dos nomes para maiúsculas, pois o software faz distinção entre letras maiúsculas e minúsculas. Para isto, pode-se utilizar o comando toupper(Banco_1$Nome). Para a substituição de letras, utiliza-se a função str_replace_all - comando: Banco_1$Nome <- str_replace_all(Banco_1$Nome,” DAS “, “ “); ou, para substituir todos os conectores ao mesmo tempo, str_replace_all(Banco_1$Nome,”\ | DA |,|;|:|-| DE | E | DO | DAS | DOS | “, “ “ ).
Após esta substituição, sugere-se a exclusão dos espaços em branco entre os nomes, pois é possível que se encontrem espaços duplos entre os nomes, e isto impediria processos de vinculação determinística - comando: Banco_1$Nome <- str_replace_all(Banco_1$Nome,” “, “” ).
Esse processo de padronização das variáveis de nome do notificado, CPF, data de nascimento e nome da mãe considera a possibilidade de pequenas inconsistências no preenchimento dessas informações pelos notificantes, nos diferentes sistemas de informações.
Após a limpeza e padronização dessas informações, é possível explorar o banco de dados para verificação de registros duplicados. A função distinct pode ser utilizada para excluir registros duplicados; porém, a exclusão ou não desses registros duplicados deve ser discutida antecipadamente, considerando-se o objetivo do resultado da vinculação de dados.
Previamente à vinculação, também deve ser estabelecido quantas chaves serão utilizadas no processo. A combinação de diferentes chaves, como a chave “Nome_paciente” combinada com a chave “Data_nascimento”, acarretará um processo de vinculação mais específico, prezando-se por maior número de registros verdadeiros-positivos. A utilização de apenas uma chave, como “Nome_paciente”, apresentará resultados mais sensíveis, com maior presença de pareamentos falsos- -positivos. Destaca-se ainda que o software R realiza análises combinatórias para os possíveis pares; logo, se há cinco pessoas com o nome “MARIA DOS ANJOS” em cada banco de dados, o software retornará um banco vinculado com 25 resultados. Devido a isso, sugere-se sempre a utilização de pelo menos duas variáveis-chave de vinculação.
A decisão de se utilizar mais de duas chaves para a vinculação deve estar embasada em análises de qualidade dos bancos de dados, pois o processo determinístico pode ser afetado por dados digitados incorretamente; por exemplo, quando se encontram datas de nascimento diferentes, mas, mediante análises manuais, o pesquisador consegue identificar serem as mesmas, embora tenham sido inseridas com algum erro de digitação. Dessa forma, pode ser interessante utilizar métodos mais sensíveis, desde que acompanhados por limpezas manuais de possíveis pareamentos verdadeiros-negativos (Quadro 1).
Quadro 1 - Exemplos de variáveis-chave utilizadas para vinculação, e possíveis resultados
| Banco de dados 1 | Banco de dados 2 | Resultado | Avaliação | ||||
|---|---|---|---|---|---|---|---|
| Nome_pacientea | Data_nascimentoa | Nome_mae | Nome_pacientea | Data_nascimentoa | Nome_mae | ||
| MariaAnjos | 27-09-1994 | LurdesSilva | MariaAnjos | 27-09-1994 | LurdesSilva | Pareado | Verdadeiro positivo |
| MariaAnjos | 27-09-1994 | LurdesSilva | MariaAnjos | 27-09-1994 | AnaCleide | Pareado | Falso positivo |
| MariaAnjos | 27-09-1994 | LurdesSilva | MariaAnjos | 13-03-2001 | MariaDores | Não pareado | Verdadeiro negativo |
| MariaAnjos | 27-09-1994 | LurdesSilva | MariaAnjos | 27-09-1894 | LurdesSilva | Não pareado | Falso negativo |
a) Campo utilizado como chave.
Vinculação de dados
A vinculação determinística identifica pares de registros concordantes, a partir de um determinado conjunto de regras.21 Ela é indicada quando os bancos de dados a serem trabalhados apresentarem uma variável identificadora comum ou um conjunto de variáveis com boa qualidade de preenchimento.10,22,23
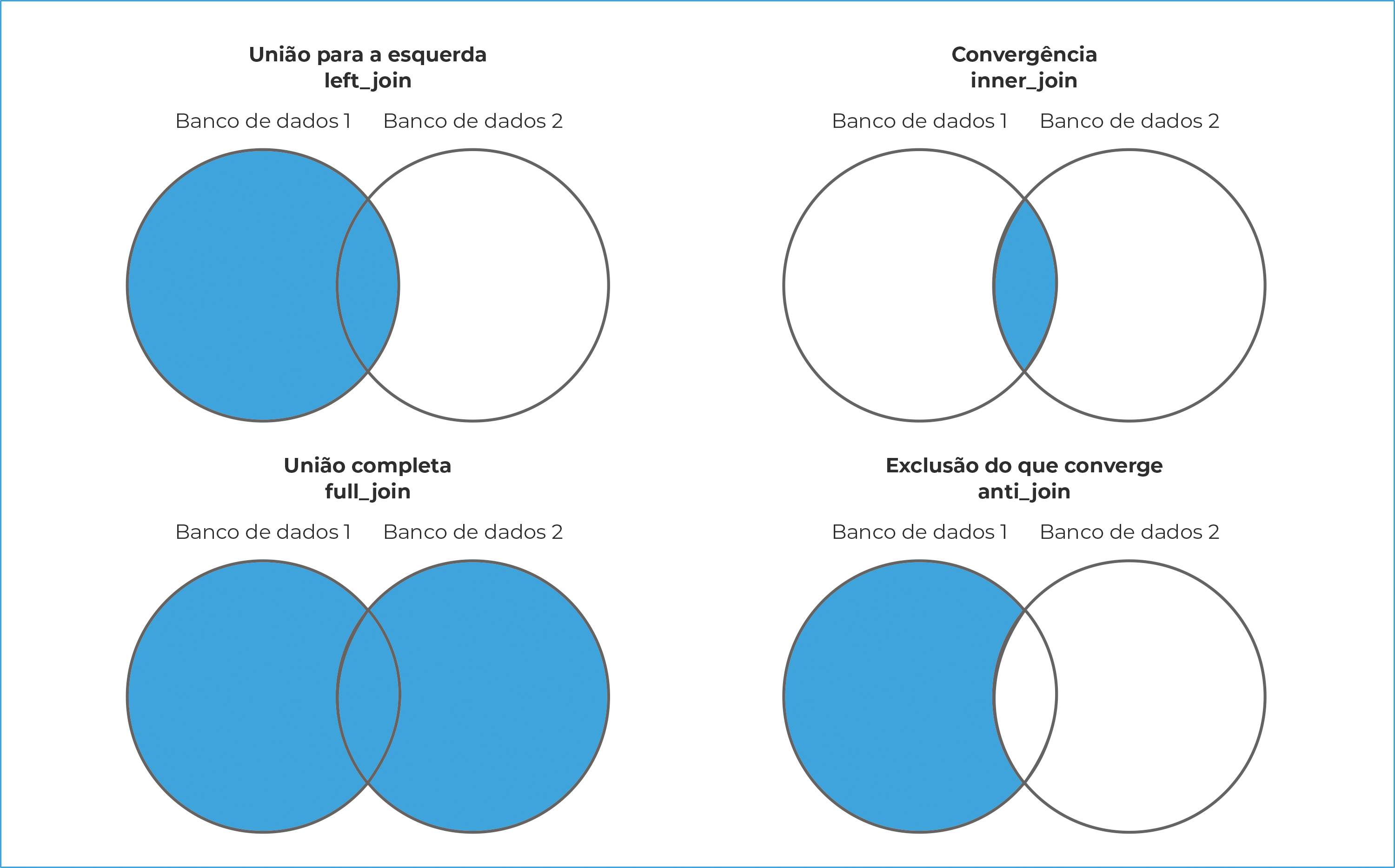
Utilizando-se o software R, é possível realizar diferentes formas de vinculação. As mais frequentes, descritas a seguir, são exemplificadas no Quadro 2. As funções a serem utilizadas são “left_join”, “inner_join”, “full_join” e “semi_join”.24 A função left_join alimenta o Banco de dados 1 com informações do Banco de dados 2. A função inner_join retorna apenas as informações com chaves comuns aos dois bancos, ou seja, apenas os registros concordantes. A função full_join junta ambos os bancos de dados, sem perda de informações. A função anti_join retorna os registros do Banco de dados 1 que não encontraram pareamento com o Banco de dados 2 (Figura 1).
Para que o funcionamento das funções descritas previamente seja facilitado, indica-se que as variáveis-chave para a vinculação recebam exatamente o mesmo nome; caso contrário, as funções precisarão da especificação dos diferentes nomes das chaves.
Após a conclusão da vinculação, o banco de dados estará pronto para ser explorado e analisado. Os principais pacotes para análise desses dados já terão sido carregados indiretamente, pelo carregamento do pacote tidyverse.13
Simulação do processo de vinculação determinística
Para a simulação da vinculação determinística, foram criados dois bancos de dados (data frames) por meio da função “randomNames” do pacote “randomNames”.14 O Banco_1 foi criado com 10 mil observações, e o Banco_2, com 500 mil observações. Nestes bancos, foram incluídas variáveis simuladas para “Nome” (nome e sobrenome), “Nome da mãe” (apenas o primeiro nome), “Data de nascimento”, “Nome do Banco” e outras duas variáveis teste (variável teste X, teste Y, Teste W, e Teste Z), totalizando seis variáveis em cada banco de dados. O script R para criação dos bancos simulados está disponível no material suplementar (https://github.com/kleydmann/Modelo_Vinculacao_deterministica.git).
IMPLEMENTAÇÃO DA VINCULAÇÃO
Roteiro de dados:
Instalação e carregamento dos pacotes necessários:
install.packages(“tidyverse”)
install.packages(“lubridate”)
install.packages(“abjutils”)
library(tidyverse)
library(lubridate)
library(abjutils)
Definição de diretório:
setwd(“C:/Users/User/Desktop/Pasta de trabalho”)
Importação dos bancos de dados para o ambiente R:
Banco_1 <- read.csv2(“Banco_1.csv”)
Banco_2 <- read.csv2(“Banco_2.csv”)
Exclusão de variáveis, se necessário:
Banco_1$X_Y <- NULL
Banco_2$X_Z <- NULL
Seleção das variáveis de interesse, se necessário:
Banco_1 <- select( Banco_1, Nome, Nome_mae, DT_NASC, Banco, variavel_X)
Banco_2 <- select( Banco_2, Nome, Nome_mae, DT_NASC, Banco, variavel_Z)
Após o tratamento dos dados, o Banco_1 e o Banco_2 foram compostos por 10 mil e 500 mil observações, respectivamente, e cinco variáveis cada um.
Verificação da codificação das variáveis-chave:
> class(Banco_1$Nome)
[1] “character”
> class(Banco_1$Nome_mae)
[1] “character”
> class(Banco_1$DT_NASC)
[1] “Date”
> class(Banco_2$Nome)
[1] “character”
> class(Banco_2$Nome_mae)
[1] “character”
> class(Banco_2$DT_NASC)
[1] “Date”
Convertendo tipo da variável de “Data de nascimento”:
Banco_1$DT_NASC <- ymd(Banco_1$DT_NASC)
Banco_2$DT_NASC <- ymd(Banco_2$DT_NASC)
Transformando as letras em maiúsculas:
Banco_1$Nome <- toupper(Banco_1$Nome)
Banco_1$Nome_mae <- toupper(Banco_1$Nome_mae)
Banco_2$Nome <- toupper(Banco_2$Nome)
Banco_2$Nome_mae <- toupper(Banco_2$Nome_mae)
Tratamento das variáveis “Nome” e “Nome_mae” do Banco_1 e Banco_2 (remoção de palavras conectoras, preposições, acentos gráficos e espaços duplos):
Banco_1$Nome <- str_replace_all(Banco_1$Nome,”\ | DA |,|;|:|-| DE | E | DO | DAS | DOS | “, “ “ )
Banco_1$Nome <- rm_accent(Banco_1$Nome)
Banco_1$Nome_mae <- str_replace_all(Banco_1$Nome_mae,”\ | DA |,|;|:|-| DE | E | DO | DAS | DOS | “, “ “ )
Banco_1$Nome_mae <- rm_accent(Banco_1$Nome_mae)
Banco_2$Nome <- str_replace_all(Banco_2$Nome,”\ | DA |,|;|:|-| DE | E | DO | DAS | DOS | “, “ “ )
Banco_2$Nome <- rm_accent(Banco_2$Nome)
Banco_2$Nome_mae <- str_replace_all(Banco_2$Nome_mae,”\ | DA |,|;|:|-| DE | E | DO | DAS | DOS | “, “ “ )
Banco_2$Nome_mae <- rm_accent(Banco_2$Nome_mae)
Remoção de espaços em branco:
Banco_1$Nome <- str_replace_all(Banco_1$Nome,” “, “” )
Banco_1$Nome_mae <- str_replace_all(Banco_1$Nome_mae,” “, “” )
Banco_2$Nome <- str_replace_all(Banco_2$Nome,” “, “” )
Banco_2$Nome_mae <- str_replace_all(Banco_2$Nome_mae,” “, “” )
Vinculação determinística por método inner_join (apenas registros congruentes em ambas as bases)
Utilização de 1 chave:
Banco_vinculado_1_chave <- inner_join(Banco_1,Banco_2, by = “Nome”)
Utilização de 2 chaves:
Banco_vinculado_2_chaves <- inner_join(Banco_1,Banco_2, by = c(“Nome”,”Nome_mae”))
Utilização de 3 chaves:
Banco_vinculado_3_chaves <- inner_join(Banco_1,Banco_2, by = c(“Nome”,”Nome_mae”,”DT_NASC”))
O processo de vinculação determinística inner_join utilizando uma única variável- -chave (“Nome”) resultou em um banco de dados com 40.108 possíveis pares e nove variáveis. A utilização de apenas uma chave resultou em maior quantidade de possíveis pares do que o total de registros existentes no Banco de dados 1, isto devido às análises combinatórias que o software R realiza durante a vinculação.
Quadro 2 - Exemplos de funções para vinculação de dados do software R
| Método | Quantidade de chaves | Funções |
|---|---|---|
| left_join | 1 | left_join(Banco_1, Banco_2, by = " Nome_paciente ") |
| 2 | left_join(Banco_1, Banco_2, by = c("Nome_paciente ", "Data.de.Nascimento")) | |
| 3 | left_join(Banco_1, Banco_2, by = c("Nome_paciente ", "Data.de.Nascimento", "nome.da.mae")) | |
| inner_join | 1 | inner_join(Banco_1, Banco_2, by = "Nome_paciente ") |
| 2 | inner_join(Banco_1, Banco_2, by = c("Nome_paciente ", "Data.de.Nascimento")) | |
| 3 | inner_join(Banco_1, Banco_2, by = c("Nome_paciente ", "Data.de.Nascimento", "nome.da.mae")) | |
| full_join | 1 | full_join(Banco_1, Banco_2, by = "Nome_paciente ") |
| 2 | full_join(Banco_1, Banco_2, by = c("Nome_paciente ", "Data.de.Nascimento")) | |
| 3 | full_join(Banco_1, Banco_2, by = c("Nome_paciente ", "Data.de.Nascimento", "nome.da.mae")) | |
| anti_join | 1 | anti_join(Banco_1, Banco_2, by = "Nome_paciente ") |
| 2 | anti_join(Banco_1, Banco_2, by = c("Nome_paciente ", "Data.de.Nascimento")) | |
| 3 | anti_join(Banco_1, Banco_2, by = c("Nome_paciente ", "Data.de.Nascimento", "nome.da.mae")) |
Ao se utilizarem duas variáveis-chave (“Nome” e “Nome da mãe”), foram encontrados 112 pares (1,12%). Ao se adicionar a terceira variável-chave, “Data de nascimento”, apenas dois (0,02%) pares foram identificados.
DISCUSSÃO
Embora o relacionamento de banco de dados, também conhecido como linkage, tenha sido descrito em diversos estudos25-28 como uma técnica relevante para melhorar a qualidade das informações em saúde, sua utilização ainda não é amplamente difundida nos ambientes da vigilância em saúde.
Entre as principais vantagens do linkage para os serviços de saúde, estão (i) a possibilidade de aprimorar as informações provenientes dos sistemas de informações, com resgate de informações incompletas, e (ii) a identificação de erros no preenchimento dos dados. Maia, Souza e Mendes25 verificaram que a técnica de linkage contribui para o aprimoramento da qualidade dos dados de mortalidade infantil em cinco cidades brasileiras, com 92% dos campos incompletos do SIM e do Sinasc recuperados. Dados sobre tuberculose no município do Rio de Janeiro foram qualificados, com redução de inconsistências no banco de dados após linkage com utilização dos bancos de dados do SIM e dados sobre aids (Sinan).28
Quanto à abordagem metodológica deste trabalho, não se utilizou a abordagem probabilística, por esta requerer definições de regras de pareamento e delimitação de pontos de corte para os índices de similaridade, fazendo-se assim necessário o desenvolvimento de um estudo específico para tais técnicas.23
As estratégias de linkage abordadas neste estudo tendem a apresentar um baixo número de identificação de pares verdadeiros, ao se utilizarem muitas variáveis-chave no processo de pareamento. Sendo assim, talvez seja interessante utilizar códigos fonéticos combinados com outras variáveis, uma alternativa possível para aumentar a sensibilidade do método.
No entanto, é essencial a definição de conjuntos de regras que permitam a utilização de chaves de vinculação que sejam precisas, estáveis ao longo do tempo e comuns às diferentes bases de dados de interesse.20
As quatro diferentes funções utilizadas para o linkage neste estudo permitem diferentes formas de exploração dos dados após a vinculação. O método left_join e o método inner_join são mais frequentemente utilizados, pois adotam o primeiro banco de dados como referência e o segundo como fonte de novas informações. Assim, o método left_join pode, por exemplo, ser utilizado para a complementação de informações referentes a “Ocupação”, uma variável que não se encontra em todas as fichas de notificação do Sinan, embora esteja presente em alguns sistemas de informações do Ministério do Trabalho e Previdência. O método inner_join, por exemplo, pode ser utilizado para parear informações de notificações de casos do Sinan com notificações de óbitos presentes no SIM, permitindo a análise específica de casos que evoluíram a óbito.
A limpeza prévia dos dados a serem pareados permite ampliar a acurácia geral do algoritmo de linkage empregado, dado que alguns bancos apresentam má qualidade de dados.
É importante mencionar que os procedimentos descritos neste trabalho possuem um nível de operacionalização e replicabilidade de maior simplicidade. Porém, a depender da complexidade da vinculação que se planeja, outros pacotes, como o “RecordLinkage”,29 e métodos podem ser mais adequados.
De todo modo, é preciso estar atento aos pareamentos entre bancos que possuam registros duplicados ou registros diferentes para uma mesma pessoa, pois as funções descritas neste trabalho resultam em diferentes possibilidades de análises combinatórias frente a registros idênticos.
As limitações descritas aqui, sobre o método e as técnicas gerais de vinculação de dados, estão principalmente relacionadas à possibilidade de erros sistemáticos provenientes da utilização de bancos de dados secundários, desde que a utilização de bancos de dados de grande magnitude torna onerosa a tarefa de conferência manual de possíveis pares falsos-positivos. Ademais, a limitação do software R no gerenciamento de memória interna é um aspecto que pode dificultar a execução da vinculação. Logo, é essencial que se discuta previamente o processo de vinculação, visando diminuir a possibilidade de vieses de seleção e de problemas operacionais do software.
A qualidade do banco de dados vinculado é dependente da qualidade dos bancos de dados originais. Dessa forma, é importante que seja feita uma avaliação prévia da qualidade dos dados, para se conhecer as deficiências e limitações de cada banco de dados e, se possível, corrigi-las antes da vinculação. Esta é uma etapa importante no pré-processamento analítico, em análise de dados.
CONSIDERAÇÕES FINAIS
As análises de bancos de dados vinculados apresentam-se como uma ferramenta válida e útil aos serviços de saúde, principalmente os que configuram as esferas estaduais e federais de governo.
Estes métodos permitem a realização de estudos descritivos e guardam potencial para subsidiar estudos analíticos, bem como fornecer informações que podem contribuir no desenvolvimento de ações estratégicas em saúde e no fomento de políticas públicas de saúde voltadas a populações mais vulneráveis. A incorporação do método linkage na rotina dos serviços de saúde pode ser uma ferramenta a se utilizar, contribuindo para a implantação de ações mais adequadas, visando à melhoria da vigilância em saúde.
Por fim, a necessidade de se implantarem processos de vinculação de dados destaca a fragilidade da interoperabilidade entre os sistemas de informações governamentais. Tal deficiência precisa ser trabalhada, promovendo melhor integração entre sistemas de informações, tanto da saúde como de outras áreas do Estado.










 texto em
texto em