Serviços Personalizados
Journal
Artigo
Indicadores
-
 Citado por SciELO
Citado por SciELO
Links relacionados
-
 Similares em
SciELO
Similares em
SciELO
Compartilhar
Revista Pan-Amazônica de Saúde
versão impressa ISSN 2176-6215versão On-line ISSN 2176-6223
Rev Pan-Amaz Saude v.1 n.2 Ananindeua jun. 2010
http://dx.doi.org/10.5123/S2176-62232010000200012
ARTÍCULO ORIGINAL
Caracterización genética parcial del hantavirus Seoul en ratas provenientes de Buenos Aires, Argentina, y generación de un antígeno a partir de la nucleoproteína recombinante del virus Seoul
Paula Julieta PadulaI; Valeria Paula MartínezI; Gerardo Rubén CuetoII; Regino CaviaII; Olga Virginia SuárezII
IDepartamento de Virología, Instituto Nacional de Enfermedades Infecciosas, Administración
Nacional de Laboratorios e Institutos de Salud "Dr. Carlos G. Malbrán",
Buenos Aires, Argentina
IILaboratorio de Ecología
de Roedores, Departamento de Ecología Genética y Evolución,
Facultad de Ciencias Exactas y Naturales, Universidad de Buenos Aires, Buenos
Aires, Argentina
Endereço para
correspondência
Correspondence
Dirección para correspondencia
RESUMEN
La fiebre hemorrágica con síndrome renal (FHSR) es una enfermedad grave, caracterizada por fiebre, hemorragia, falencia renal y trombocitopenia. Al menos siete hantavirus causan la FHSR: Hantaan, Seoul (SEOV) (de distribución global), Dobrava-Belgrade, Saaremaa, Amur, Thailand y Puumala. Para investigar la epidemiología de la FHRS y la transmisión viral en Argentina, creamos un plásmido procariotas que "codifica" la nucleoproteína recombinante del virus SEOV de 430 aminoácidos. Luego de la expresión, la nucleoproteína recombinante fue probada como antígeno para uso en ensayo inmunoenzimático (ELISA) para diagnóstico de la infección. Para determinar el nivel actual de transmisión viral en poblaciones de ratas marrones o ratas (Rattus norvegicus) capturadas en la ciudad de Buenos Aires, Argentina, analizamos tejidos de ratas seleccionadas para ser serológicamente positivas para el virus SEOV, y su genoma viral fue detectado luego de sometido a RT-PCR utilizando primers específicos para dos fragmentos de proteínas Gn y Gc codificadas por el segmento M. El genoma viral fue detectado en 11 de las 21 ratas seropositivas (52,4%), previamente capturadas en dos parques. El análisis secuencial de una región génica (333 nt) del segmento M "codificador" de la proteína Gc presentó un 97% y un 96% de similitud con las cepas de SEOV colectadas en Baltimore y en Brasil, respectivamente. Los datos genéticos listados confirman la información de que hay una diversidad muy pequeña entre las cepas del virus SEOV.
Palabras clave: Hantavirus; Virus Seoul; Ratas; Células Procarióticas; Proteínas Recombinantes; Prueba ELISA.
INTRODUCCIÓN
Los hantavirus (familia Bunyaviridae, género Hantavirus) son virus transmitidos por roedores que causan dos graves enfermedades. En Eurasia, la fiebre hemorrágica con síndrome renal (FHSR) es una enfermedad infecciosa grave causada por, al menos, cuatro hantavirus antigénica y genéticamente distintos clasificados por diferentes serotipos: Hantaan (HTNV), Seoul (SEOV), Dobrava/Belgrado (DOB), y Puumala (PUUV)21. En las Américas, los hantavirus asociados a la sigmodontinae, como el virus Sin Nombre (SNV), en América del Norte, y el virus Andes (ANDV), en América del Sur, causan síndrome pulmonar por hantavirus17,14. Su genoma de RNA presenta triple cadena, con segmentos de cinta simple de polaridad negativa, que "codifican" el RNA polimerasa dependiente de RNA, dos glicoproteínas emergiendo del envelope (Gn y Gc) y una proteína de la nucleocápside (NP)20.
En la naturaleza, cada hantavirus tiene como reservorio predominante a roedores de diferentes especies, y las enfermedades resultantes de infecciones por esos virus están confinadas a la región correspondiente a la distribución de su huésped roedor22. Sin embargo, como las especies del género Rattus son cosmopolitas, el virus SEOV tiene la potencialidad de causar la enfermedad en humanos en todo el mundo debido a la distribución de sus huéspedes infectados, las ratas negras (R. rattus) y las ratas comunes o ratas pardas (R. norvegicus)13, por el transporte internacional de mercaderías. Existen actualmente pocos relatos de casos confirmados de infecciones humanas por SEOV fuera del continente asiático, incluyendo ocurrencias en los EUA7 y en Brasil9. Hasta el presente, el registro de FHSR resultantes de la infección por SEOV ha sido restricto principalmente a los países asiáticos19. En Buenos Aires, el SEOV ha sido detectado serológicamente en ratas desde 198512,23,26; sin embargo, ningún caso de FHSR causada por SEOV ha sido registrado23. Recientemente, un estudio sobre la seroprevalencia de la infección por SEOV en ratas de la Ciudad de Buenos Aires reveló una positividad de 11,9%2, aunque el genoma viral no fue caracterizado.
Debido a la naturaleza altamente patógena de los hantavirus, su replicación lenta y su baja y variable productividad en cultivo de células, se han producido proteínas recombinantes de hantavirus para utilización como antígenos en pruebas serológicas, incluyendo pruebas para SEOV10,27,25,5,4,18,1.
En esta investigación, presentamos la primera evidencia genética de SEOV en ratas en la Ciudad de Buenos Aires, Argentina. Creamos también un antígeno para la proteína de la nucleocápside recombinante de SEOV (rNP) para uso en pruebas serológicas.
MATERIALES Y MÉTODOS
ANIMALES CAPTURADOS EN AMBIENTE SALVAJE
De 2003 a 2005, ratas salvajes fueron capturadas en diversas localidades en la Ciudad de Buenos Aires, Argentina, tales como parques urbanos con más de 20 ha., áreas residenciales urbanas con alta densidad poblacional y villas. Durante este estudio, se capturaron 151 ratas y 33 ratas negras, en un total de 14,088 trampas nocturnas2.
Se colectaron muestras de sangre de todos los especimenes capturados vía punción cardiaca para análisis serológica. Se removieron muestras de tejido del pulmón, hígado y riñón de cada roedor y se las almacenó en nitrógeno líquido hasta el momento de la prueba.
CLONACIÓN, EXPRESIÓN Y PURIFICACIÓN DEL RNP DEL VIRUS SEOV
Para la clonación, usamos el vector pGEM-T y la cepa de Escherichia coli DH5a cultivada en medio Luria-Bertani. El stock viral de SEOV Sapporo de cepas de ratas (gentilmente suministrado por Jay Hooper y Connie Schmaljohn, del United States Army Medical Research Institute of Infectious Diseases, Fort Detrick, Frederick, MD) fue ampliado en células Vero, y el RNA viral se extrajo del sobrenadante de células. Para generar un plasmideo conteniendo la ORF completa de la proteína N, realizamos una RT-PCR con primers sintetizados para contener los sitios de restricción, sucediendo el inmediato anelamiento por sobre el codón de inicio N e inmediatamente debajo en el codón de interrupción N. El plasmideo pGEM-T ligado al cDNA fue transformado en E. coli DH5α.
Para la expresión de la proteína recombinante, utilizamos el pRSET B (Invitrogen Life Technologies) para transformar el plasmideo en la cepa de E. coli BL21(DE3), siguiendo las orientaciones del fabricante, y ajustamos la ampicilina para mutantes resistentes. Luego de la lisis celular y el centrifugado, el sobrenadante fue purificado a través de cromatografía de afinidad con Ni. Las proteínas purificadas se analizaron por electroforesis en gel de poliacrilamida 10% con dodecil sulfato de sodio (SDS-PAGE) y glicina.
ENSAYO INMUNOABSORBENTE LIGADO A ENZIMA
Se realizó un ensayo inmunoabsorbente ligado a enzima (ELISA) en muestras de sangre total para detectar anticuerpos IgG, como descrito anteriormente para el virus ANDV18. En seguida, las placas fueron cubiertas durante la noche a 4° C con rNP de SEOV y antígeno recombinante control o células Vero E6 infectadas con SEOV y células Vero E6 no infectadas. Las muestras se diluyeron a 1:200 en solución salina tamponada con fosfato con Tween 20 y agregadas en duplicado a pozos revestidos con antígeno conteniendo células Vero E6 infectadas o no infectadas. Las placas fueron lavadas con la misma solución tampón e incubadas a 37° C por 1 h con anticuerpos anti-inmunoglobulina G de rata conjugado a la fosfatasa alcalina (H + L; Kirkegaard and Perry Laboratories, Gaithersburg, MD). Las placas se incubaron por 1 h a 37° C, y se adicionó el sustrato para peroxidasa. La densidad óptica (DO) fue de 405 nm, y la DO media para cada grupo de duplicados de Vero E6 no infectadas o antígeno recombinante control se sustrajo de la DO media de cada grupo de duplicados de Vero E6 infectadas o antígenos rNP de SEOV, respectivamente. Las muestras fueron consideradas positivas cuando la diferencia entre los valores de DO fue mayor que 0,3. Debido al hecho de que los hantavirus transmitidos por roedores de la familia Sigmodontinae tienen circulación reportada en Buenos Aires y áreas vecinas, también analizamos muestras de suero de ratas con valores bajos de ELISA-SEOV, utilizando antígeno recombinante de ANDV, como previamente descrito18.
El título fue definido como la recíproca de la mayor dilución cuya DO alcanzaba 0,3 o más.
AISLAMIENTO DEL RNA, AMPLIFICACIÓN, SECUENCIACIÓN Y ANÁLISIS DE ADN
El RNA total extraído de tejidos de pulmón o riñón de los roedores con el reactivo Trizol (Invitrogen Life Technologies®) fue sometido a transcripción reversa utilizando AMV (Promega Corp.®) y primers específicos, de acuerdo a las recomendaciones del fabricante. Los procedimientos de RT-PCR hemi-nested y single round tuvieron como finalidad amplificar dos fragmentos parciales del RNA hantaviral del segmento M. Para amplificar el fragmento Gn del área génica 437 nt (6 a 442), utilizamos los primers P0 (5'-TAGTAGTAGACTCCGC-3 ') con P10 (5'- GTTTGATTACAGGCCAGATCATAACA-3') para la primera etapa y P57 (5'- GACTCCGCAAGAAGAAGC - 3') con P10 para la segunda etapa. Se obtuvo una secuencia de 385 nt. Para el análisis del fragmento Gc (333 nt de 1984 a 2316), fueron secuenciados del punto de vista genético24. Todas las posiciones del segmento genómico se refirieron a la cepa del virus SEOV Sapporo. Los productos de la PCR fueron separados por medio de electroforesis en gel de agarosa, teñida con bromuro de etidio y visualizados bajo luz UV. Los productos fueron purificados y secuenciados directamente utilizando un secuenciador automático de ADN (ABI PRISM® 3100- Avant Genetic Analyzer System, Perkin-Elmer, USA).
Los números de acceso al Genbank de las cepas de referencia previamente publicadas son: AF324901 (ANDV); AF00578 virus Laguna Negra (LNV); L25783 (SNV); M29979 (PUUV); NC005228 (TULV); L33685 (DOBV); M14627 (HTNV); SEOV cepa U00151 (Baltimore), SEOV cepa U00460 (Brasil), cepas chinas de SEOV: DQ133505 (BjHD01), YS32 EF205404 (YS32), AF035832 (HB55), EF2053277 (HLD65), SEOV adquirido en laboratorio AF458104 (IR461); SEOV cepa U00465 (Houston), SEOV cepa M34882 (Sapporo), SEOV cepa U00463 (Egipto). (ANDV); AF00578 virus Laguna Negra (LNV); L25783 (SNV); M29979 (PUUV); NC005228 (TULV); L33685 (DOBV); M14627 (HTNV); SEOV cepa U00151 (Baltimore), SEOV cepa U00460 (Brasil), cepas chinas de SEOV: DQ133505 (BjHD01), YS32 EF205404 (YS32), AF035832 (HB55), EF2053277 (HLD65), SEOV adquirido en laboratorio AF458104 (IR461); SEOV cepa U00465 (Houston), SEOV cepa M34882 (Sapporo), SEOV cepa U00463 (Egipto).
RESULTADOS
CARACTERIZACIÓN Y ANÁLISIS DE RNP DEL SEOV EXPRESADO EN BACTERIAS
Utilizamos un vector pRSET B en sistema inducible BL21, en el cual el rNP del virus SEOV de 430 aminoácidos expresa y purifica muy bien. La secuenciación nucleotídica del producto de la expresión por vector reveló la serie de bases esperada. La SDS-PAGE reveló un rNP altamente purificado, con peso molecular de cerca de 51 kDa. La producción de rNP del SEOV por 500 mL de células de E. coli varió de 3 a 4 mg de proteína.
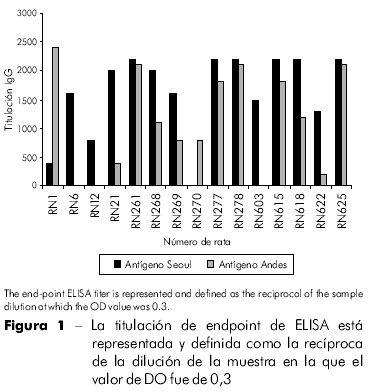
TEl rNP recién generado fue evaluado con vista a su utilización como un antígeno para diagnóstico en pruebas IgG-ELISA. Los estándares de reactividad del rNP correspondieron a los de virus auténticos de cultivo de células Vero E6 (datos no presentados). Para analizar la reactividad cruzada de virus ANDV y SEOV, fueron analizadas muestras de suero de ratas en ELISA utilizando ambos antígenos de rNP. El estándar de reactividad del rNP del virus ANDV se mostró diferente del rNP del virus SEOV (Figura 1). Los valores de DO variaron en las diferentes muestras en la dilución sérica (1:200) utilizada para los valores de endpoint de titulación. Las muestras de suero con DO baja no pudieron ser detectadas por rNP del ANDV, mientras que en muestras con titulación alta de IgG, los rNPs no pudieron diferenciar serológicamente las infecciones causadas por el ANDV de las causadas por SEOV. Tres muestras positivas de SOEV obtenidas por medio de RT-PCR, con altos valores de DO no pudieron ser distinguidas para los rNPs de ANDV y SEOV.
SELECCIÓN DE ROEDORES PARA LA PRESENCIA DE GENOMA VIRAL
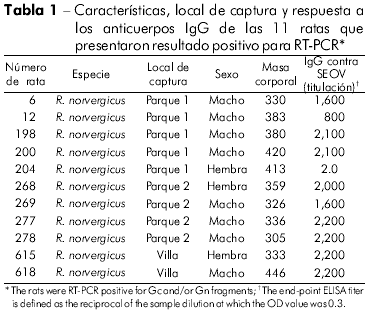
De las 151 ratas capturadas en Buenos Aires, 21 ratas (13,9 %) fueron seropositivas para el antígeno rNP de SEOV. Los ratones serológicamente positivos fueron analizados para SEOV por RT-PCR usando primers específicos de 2 fragmentos del segmento M, que codifica las proteínas Gn y Gc. El genoma viral se detectó en los pulmones de 11 (52,4%) de las 21 ratas seropositivas capturadas en dos parques (Tabla 1). Ocho de las 11 ratas eran de sexo masculino (72,7%), y todos mostraron respuesta adecuada a los anticuerpos. Como era esperado, ningún producto fue amplificado de los órganos de los seis roedores seronegativos. En nuestras pruebas ELISA, dos de las ratas presentaron titulación alta contra el antígeno de ANDV y titulación muy baja contra el antígeno rNP de SEOV. No sabemos si estas ratas habían tenido contacto previo con roedores Oligoryzomys spp. infectados. Infelizmente, ningún genoma viral fue amplificado de esos animales.
COMPARACIÓN GENÉTICA Y ANÁLISIS FILOGENÉTICO
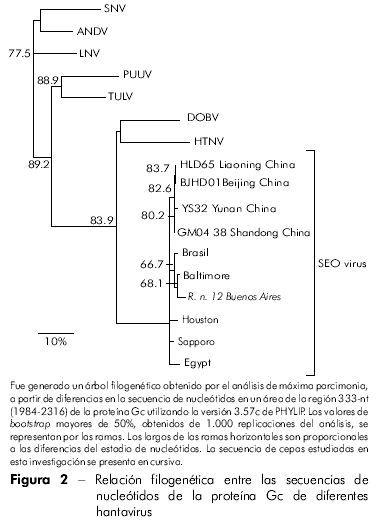
Entre los 11 productos amplificados de Gn, seis cADNs representativos de dos locales de captura fueron secuenciados. La comparación pareada de secuencias de un fragmento Gn (385 nt) entre tres ratas (RN 12, RN 198 y RN 200) de un parque, y tres de otro parque (RN204, RN277 e RN278) presentó 100% de identidad entre las tres ratas de cada grupo (Tabla 2). Ratas de los dos parques (RN12 e RN277) mostraron una identidad de nucleótidos de 96,3%. La comparación entre las secuencias de aminoácidos deducidas de las seis ratas reveló un 100% de identidad. La comparación de los Gn de las ratas de ambos grupos con otros infectados con SEOV mostró la mayor tasa de identidad nucleotídica con las cepas chinas IR461 y HB55 (AF458104 y AF035832). Las comparaciones secuenciales de un fragmento Gc 333-nt de una rata negra proveniente de Argentina (RN12) con otras de SEOV presentaron mayores tasas de identidades nucleotídicas con las cepas provenientes de Baltimore, EUA, y de Brasil (97% y 96%, respectivamente; Tabla 3). Los análisis filogenéticos basados en el fragmento Gc 333-nt generado por el método de análisis de parsimonia colocaron a la cepa RN12 del virus SEOV de Buenos Aires junto a las cepas provenientes de Baltimore y Brasil (Figure 2).


DISCUSSION
En este estudio registramos por primera vez la detección de material genético del virus SEOV en ratas seropositivas capturadas en la Ciudad de Buenos Aires, Argentina. La presencia de SEOV en Buenos Aires no causó sorpresa, ya que estudios anteriores habían reportado una seropositividad para SEOV de 31%23. Sus huéspedes, R. norvegicus y R. rattus, se hallan en el país y la distribución de este virus está registrada en todo el mundo. No se detectó ninguna rata negra seropositiva; no se verificó una distribución igualitaria de ratas seropositivas en los 5 diferentes sitios investigados en la Ciudad de Buenos Aires, donde las tasas de seroprevalencia variaron entre 0% y 26,1%2. La prueba serológica es una medida indirecta de la infección viral, y se ve afectada de forma variable por el estatus inmunológico del huésped; sin embargo, es el método más frecuentemente utilizado para evaluar la infección por hantavirus en la sangre de roedores.
Anteriormente, demostramos que el análisis ELISA basado en rNP de ANDV presenta buenos resultados para la detección de anticuerpos virus-específicos en pacientes y roedores con ANDV. En esta investigación, se desarrolló el ensayo serológico para uso en el diagnóstico de SEOV. Demostramos que la antigenicidad del rNP completo del SEOV era fuerte lo bastante como para ser utilizado en un ensayo inmunoenzimático. El ELISA basado en el uso del antígeno suministró resultados que corroboraron los resultados obtenidos utilizando fluidos de cultivo de células infectadas con el SEOV. El ensayo podría detectar la reactividad de los anticuerpos IgG en ratas y en las muestras de pacientes control con SEOV de otras partes del mundo (datos no presentados). También analizamos las muestras de suero de ratas con bajos valores en ELISA para SEOV utilizando el antígeno rNP del ANDV, como previamente descrito18, una vez que existen registros de virus cuyos huéspedes son de la subfamilia Sigmodontinae circulando en la ciudad de Buenos Aires15. En un estudio latitudinal realizado en áreas naturales del Chile continental, de 178 ratas negras analizadas, apenas uno fue reactivo en una prueba serológica ELISA basado en ANDV16.
La detección de anticuerpos no indica necesariamente que el roedor esté infectado o sea infeccioso, pero suministra evidencia indirecta del actual nivel de transmisión del virus. En áreas en donde ratas dividen el habitat con animales del género Sigmodontinae, como en las áreas periféricas de Buenos Aires, resultados serológicos positivos podrían representar un spillover accidental de virus semejantes al ANDV (AND-lifce). Consecuentemente, el suero de roedores con anticuerpos contra otros hantavius patogénicos o no patogénicos, pueden llevar a resultados positivos (i.e., reacción cruzada) en el ensayo para el virus SEOV Por este motivo, la detección directa de ácido nucleico por RT-PCR surgió como el método de elección para varios patógenos virales. Se obtuvieron amplificaciones exitosas del genoma viral de 11 ratas seropositivas. Nuestros resultados confirman la hipótesis de que el SEOV esté circulando en la Ciudad de Buenos Aires. Este estudio constituye una prueba directa de la infección viral actual, y señala una tasa elevada de ratones infectados entre poblaciones de ratas seropositivas en la ciudad, siendo que más de la mitad de las ratas seropositivas cobijaban genomas virales detectables. Es interesante observar que la cepa del virus SEOV recientemente descrita en Buenos Aires es muy próxima a las cepas del tipo salvaje de Baltimore, EUA, y de Brasil, ambas asociadas a la rata. El puerto de Buenos Aires responde por 80% de las importaciones argentinas. Aproximadamente 50% de las ratas del sexo masculino en Baltimore, Maryland, están infectadas con SEOV3,6. Estudios con ratas debidamente marcadas y sueltos en Baltimore demuestran que las ratas del sexo masculino heridas durante la captura son más propensos a infectarse con SEOV durante la recaptura que los que no se hirieron entre las capturas6. En nuestro estudio, 72,7% de las ratas con genoma del SEOV eran del sexo masculino, aunque las heridas hayan sido raramente observadas en las ratas capturadas. Entre las poblaciones naturales de ratas, los machos con heridas más graves también están más propensos a diseminar el SEOV y presentar el ARN viral en tejidos-meta, como los pulmones, que los machos sin lesiones o con lesiones menos severas8.
Hay registros de que el SEOV ha causado enfermedades en humanos menos graves que el HTNV y el DOBV, pero todavía responsable por 25% de los casos de HFRS en Asia11. No hay registros de infecciones por SEOV en Argentina. La presencia de ratas con anticuerpos contra el virus SEOV es apenas uno de los varios factores a ser considerados cuando evaluamos los riesgos de las FHSR. Aspectos relacionados a los agentes, reservorios, medio ambiente y huéspedes interactúan de modo a determinar la probabilidad de una transmisión efectiva, bien como de infección y enfermedad causadas por el virus. Los aspectos relacionados al agente incluyen la cepa viral y la dosis mínima de infestación del hantavirus en cuestión. Los factores referentes al reservorio incluyen la infección activa (en oposición a evidencias serológicas de infecciones anteriores), la concentración de virus excretado, la densidad de roedores y la frecuencia y diseminación de las excreciones. Todos esos factores deben ser llevados en consideración cuando se vaya a evaluar la importancia de los datos a respecto de la serología de los roedores y cuando sea elaborada una planificación preventiva apropiado. Por lo tanto, la importancia de la detección del RNA de los hantavirus en ratas como agentes causadores de las FHSR en Buenos Aires permanece incierta, y son necesarias nuevas investigaciones serológicas con individuos saludables y, además estudios ambientales. No obstante, nuestros resultados indican que se necesitan estrategias de control para reducir los riesgos de infección de humanos por patógenos transmitidos por ratas.
APOYO FINANCIERO
Esta investigación fue parcialmente financiada por el Gobierno de la Ciudad de Buenos Aires
REFERENCIAS
1 Billecocq A, Coudrier D, Boue F, Combes B, Zeller H, Artois M, et al. Expression of the nucleoprotein of the Puumala virus from the recombinant Semliki Forest virus replicon: characterization and use as a potential diagnostic tool. Clin Diagn Lab Immunol. 2003 Jul;10(4):658-63. [ Links ]
2 Cueto GR, Cavia R, Bellomo C, Padula PJ, Suarez OV. Prevalence of hantavirus infection in wild Rattus norvegicus and R. rattus populations of Buenos Aires City, Argentina. Trop Med Int Health. 2008 Jan;13(1):46-51. [ Links ]
3 Easterbrook JD, Kaplan JB, Glass GE, Pletnikov MV, Klein SL. Elevated testosterone and reduced 5-HIAA concentrations are associated with wounding and hantavirus infection in male Norway rats. Horm Behav. 2007 Nov;52(4):474-81. [ Links ]
4 Elgh F, Lundkvist A, Alexeyev OA, Stenlund H, Avsic-Zupanc T, Hjelle B, et al. Serological diagnosis of hantavirus infections by an enzyme-linked immunosorbent assay based on detection of immunoglobulin G and M responses to recombinant nucleocapsid proteins of five viral serotypes. J Clin Microbiol. 1997 May;35(5):1122-30. [ Links ]
5 Feldmann H, Sanchez A, Morzunov S, Spiropoulou CF, Rollin PE, Ksiazek TG, et al. Utilization of autopsy RNA for the synthesis of the nucleocapsid antigen of a newly recognized virus associated with hantavirus pulmonary syndrome. Virus Res. 1993 Dec;30(3):351-67. [ Links ]
6 Glass GE, Childs JE, Korch GW, LeDuc JW. Association of intraspecific wounding with hantaviral infection in wild rats (Rattus norvegicus). Epidemiol Infect. 1988 Oct;101(2):459-72. [ Links ]
7 Glass GE, Watson AJ, LeDuc JW, Childs JE. Domestic cases of hemorrhagic fever with renal syndrome in the United States. Nephron. 1994;68(1):48-51. [ Links ]
8 Hinson ER, Shone SM, Zink MC, Glass GE, Klein SL. Wounding: the primary mode of Seoul virus transmission among male Norway rats. Am J Trop Med Hyg. 2004 Mar;70(3):310-7. [ Links ]
9 Iversson LB, Rosa APA, Travassos da Rosa MDB, Lomar AV, Sasaki MGM, LeDuc JW. Human infection by hantavirus in southern and southeastern Brazil. Rev Assoc Med Bras. 1994 Apr-Jun;40(2):85-92. [ Links ]
10 Kallio-Kokko H, Vapalahti O, Hedman K, Brummer-Korvenkontio M, Vaheri A. Puumala virus antibody and immunoglobulin G avidity assays based on a recombinant nucleocapsid antigen. J Clin Microbiol. 1993 Mar;31(3):677-80. [ Links ]
11 Kim YS, Ahn C, Han JS, Kim S, Lee JS, Lee PW. Hemorrhagic fever with renal syndrome caused by the Seoul virus. Nephron. 1995;71(4):419-27. [ Links ]
12 LeDuc JW, Smith GA, Pinheiro FP, Vasconcelos PFC, Rosa EST, Maiztegui JI. Isolation of a Hantaan-related virus from Brazilian rats and serologic evidence of its widespread distribution in South America. Am J Trop Med Hyg. 1985 Jul;34(4):810-5. [ Links ]
13 Lee HW. Hemorrhagic fever with renal syndrome (HFRS). Scand J Infect Dis Suppl. 1982;36:82-5.
14 Lopez N, Padula P, Rossi C, Lazaro ME, Franze-Fernandez MT. Genetic identification of a new hantavirus causing severe pulmonary syndrome in Argentina. Virology. 1996 Jun;220(1):223-6. [ Links ]
15 Martinez VP, Colavecchia SB, Garcia Alay M, Suzuki B, Trincheri A, Busto S, et al. Hantavirus pulmonary syndrome in Buenos Aires Province. Medicina (B Aires). 2001;61(2):147-56. [ Links ]
16 Medina RA, Torres-Perez F, Galeno H, Navarrete M, Vial PA, Palma RE, et al. Ecology, genetic diversity, and phylogeographic structure of Andes virus in humans and rodents in Chile. J Virol. 2009 Mar;83(6):2446-59. [ Links ]
17 Nichol ST, Spiropoulou CF, Morzunov S, Rollin PE, Ksiazek TG, Feldmann H, et al. Genetic identification of a hantavirus associated with an outbreak of acute respiratory illness. Science. 1993 Nov;262(5135): 914-7. [ Links ]
18 Padula P, Rossi CM, Della Valle MO, Martínez PV, Colavecchia SB, Edelstein A, et al. Development and evaluation of a solid-phase enzyme immunoassay based on Andes hantavirus recombinant nucleoprotein. J Med Microbiol. 2000 Feb;49(2):149-55. [ Links ]
19 Reynes JM, Soares JL, Hue T, Bouloy M, Sun S, Kruy SL, et al. Evidence of the presence of Seoul virus in Cambodia. Microbes Infect. 2003 Jul;5(9):769-73. [ Links ]
20 Schmaljohn CS, Hasty SE, Harrison SA, Dalrymple JM. Characterization of Hantaan virions, the prototype virus of hemorrhagic fever with renal syndrome. J Infect Dis. 1983 Dec;148(6):1005-12. [ Links ]
21 Schmaljohn CS, Hasty SE, Dalrymple JM, LeDuc JW, Lee HW, von Bonsdorff CH, et al. Antigenic and genetic properties of viruses linked to hemorrhagic fever with renal syndrome. Science. 1985 Mar;227(4690):1041-4.
22 Schmaljohn CS, Lee HW, Dalrymple JM. Detection of hantaviruses with RNA probes generated from recombinant DNA. Arch Virol. 1987;95(3-4):291-301. [ Links ]
23 Seijo A, Pini N, Levis S, Coto H, Deodato B, Cernigoi B, et al. Study of hantavirus seoul in a human and rodent population from a marginal area in Buenos Aires City. Medicina (B Aires). 2003;63(3):193-6. [ Links ]
24 Xiao SY, Leduc JW, Chu YK, Schmaljohn CS. Phylogenetic analyses of virus isolates in the genus Hantavirus, family Bunyaviridae. Virology. 1994 Jan;198(1):205-17.
25 Wang M, Rossi C, Schmaljohn CS. Expression of non-conserved regions of the S genome segments of three hantaviruses: evaluation of the expressed polypeptides for diagnosis of haemorrhagic fever with renal syndrome. J Gen Virol. 1993 Jun;74(Pt 6):1115-24. [ Links ]
26 Weissenbacher MC, Merani MS, Hodara VL, Villafane G, Gajdusek DC, Chu YK, et al. Hantavirus infection in laboratory and wild rodents in Argentina. Medicina (B Aires). 1990;50(1):43-6. [ Links ]
27 Zoller L, Yang S, Gott P, Bautz EK, Darai G. Use of recombinant nucleocapsid proteins of the Hantaan and nephropathia epidemica serotypes of hantaviruses as immunodiagnostic antigens. J Med Virol. 1993 Mar;39(3):200-7. [ Links ]
 Correspondência
/ Correspondence / Correspondencia:
Correspondência
/ Correspondence / Correspondencia:
Paula Julieta Padula Departamento de Virología,
Instituto Nacional de Enfermedades Infecciosas,
A.N.L.I.S. "Dr. Carlos G. Malbrán"
Av. Vélez Sarsfield 563 (1281)
Buenos Aires-Argentina
E-mail:ppadula@gmail.com
Phone/Fax: 5411 - 43013146
Recebido em / Received / Recibido en: 27/8/2009
Aceito em / Accepted / Aceito en: 30/3/2010










 texto em
texto em