
ARTIGO ORIGINAL | ORIGINAL ARTICLE | ARTÍCULO ORIGINAL
Primeira detecção de coronavírus humano associado à infecção respiratória aguda na Região Norte do Brasil
First detection of human coronaviruses associated with acute respiratory infection in Northern Brazil
Primera detección de coronavirus humano asociado a infección respiratoria aguda en la Región Norte de Brasil
]]> Akim Felipe Santos Nobre; Rita Catarina Medeiros Sousa; Mirleide Cordeiro dos Santos; Luana Soares Barbagelata; Edivaldo Costa Júnior; Deimy Ferreira Lima; Edna Maria Acunã de Souza; Wyller Alencar de Mello
Seção de Virologia, Instituto Evandro Chagas/SVS/MS, Ananindeua, Pará, Brasil
Endereço para correspondência
Correspondence
Dirección para correspondencia
RESUMO
Os coronavírus humanos (CoVh) são responsáveis por ocasionar doenças respiratórias e entéricas, sendo associados às infecções agudas e graves do trato respiratório. O objetivo deste trabalho foi identificar a ocorrência dos CoVh em pacientes com infecção respiratória aguda (IRA) na Cidade de Belém, Estado do Pará, Brasil, atendidas pelo programa de vigilância do vírus da influenza do Instituto Evandro Chagas. No período compreendido entre agosto de 2009 a março de 2011, amostras de aspirado da nasofaringe ou swab combinado (nasal e oral) obtidas de 308 pacientes com diagnóstico clínico de IRA, foram laboratorialmente investigadas na busca de evidências de infecção pelo CoVh. A metodologia adotada envolveu quatro etapas principais: a) extração do RNA viral (RNAv) do espécime clínico; b) execução da técnica de reação em cadeia mediada pela polimerase precedida de transcrição reversa (RT-PCR); c) eletroforese em gel de agarose dos produtos gerados; e d) sequenciamento genético de nucleotídeos. O processamento laboratorial de todos os espécimes revelou positividade para CoVh em uma amostra clínica dos pacientes investigados. A análise filogenética da amostra positiva permitiu classificá-la como pertencente ao subtipo OC43 de CoVh. O presente achado representa a primeira comprovação laboratorial da circulação deste agente viral na Região Amazônica. Estudos adicionais são necessários para um maior conhecimento da etiologia e epidemiologia deste agente viral em casos de IRA que ocorrem na Região Norte do Brasil.
Palavras-chave: Coronavírus; Infecções Respiratórias; Reação em Cadeia da Polimerase Via Transcriptase Reversa.
Human coronaviruses (HCoVs) are responsible for causing respiratory and enteric diseases associated with severe acute respiratory tract infections. The aim of this study was to identify the occurrence of HCoVs in patients with acute respiratory infection (ARI) in Belém, Para State, Brazil, assisted by the surveillance program of influenza viruses of Instituto Evandro Chagas. From August 2009 to March 2011, samples of nasopharyngeal aspirate or nasal and oral swabs obtained from 308 patients with clinical diagnosis of ARI were investigated in the laboratory in order to identify the HCoVs infection. The methodology involved four main steps: a) viral RNA (RNAV) extracted from the clinical specimen; b) application of reverse transcription polymerase chain reaction (RT-PCR); agarose electrophoresis gel of the generated products; and d) DNA sequencing. The laboratory processing of all specimens were positive for HCoVs in a clinical sample of patients investigated. The positive sample was classified as belonging to the subtype OC43 of HCoVs by using the phylogenetic analysis. This finding represents the first laboratory confirmation of this viral agent circulation in the Amazon Region. Additional studies are needed for a better understanding of the etiology and epidemiology of this viral agent in cases of ARI occurring in Northern Brazil.
Keywords: Coronavirus; Respiratory Tract Infections; Reverse Transcriptase Polymerase Chain Reaction.
RESUMEN
Los coronavirus humanos (CoVh) son los responsables por ocasionar enfermedades respiratorias y entéricas, siendo asociados a las infecciones agudas y graves del trato respiratorio. El objetivo de este trabajo fue el de identificar los episodios de CoVh en pacientes con infección respiratoria aguda (IRA) en la Ciudad de Belém, en el Estado de Pará, Brasil, atendidas por el programa de vigilancia del virus influenza del Instituto Evandro Chagas. En el período comprendido entre agosto de 2009 a marzo de 2011, muestras de aspirado nasofaríngeo o frotis combinado (nasal y oral) obtenidas de 308 pacientes con diagnóstico clínico de IRA, fueron investigadas en laboratorio a la búsqueda de evidencias de infección por CoVh. La metodología adoptada abarcó cuatro etapas principales: a) extracción del RNA viral (RNAv) del espécimen clínico; b) ejecución de la técnica de reacción en cadena mediada por la polimerasa precedida de transcripción reversa (RT-PCR); c) electroforesis en gel de agarosa de los productos generados; y d) secuenciación genética de nucleótidos. El procesamiento de laboratorio de todos los especímenes se reveló positivo para CoVh en una muestra clínica de los pacientes investigados. El análisis filogenético de la muestra positiva permitió clasificarla como perteneciente al subtipo OC43 de CoVh. El presente hallazgo representa la primera comprobación en laboratorio de la circulación de este agente viral en la Región Amazónica. Son necesarios estudios adicionales para un mayor conocimiento de la etiología y la epidemiología de este agente viral en casos de IRA que ocurren en la Región Norte de Brasil.
Palabras clave: Coronavirus; Infecciones del Sistema Respiratorio; Reacción en Cadena de la Polimerasa de Transcriptasa Inversa.
INTRODUÇÃO
As infecções respiratórias agudas (IRA) são causas importantes de morbidade e mortalidade em todo o mundo. Os vírus são considerados os agentes etiológicos predominantes em IRA, sejam como patógenos principais, ou predispondo indivíduos a infecções bacterianas secundárias. Manifestações clínicas graves associadas a doenças do trato respiratório inferior são frequentemente observadas em indivíduos com fatores de risco tais como: cardiopatia, pneumopatia e outras condições crônicas como diabetes, obesidade e asma1.
]]> Entre os vírus rotineiramente associados a IRA, os coronavírus humanos (CoVh) têm se destacado como agentes etiológicos emergentes, quer sejam os tipos já conhecidos como OC43 e 229E, bem como os recentemente descobertos agentes da síndrome respiratória aguda grave (SARS), o NL63 e o HKU1 descobertos em 2004 e 2005 respectivamente2,3,4.Investigações conduzidas em diferentes países têm demonstrado que estes vírus apresentam distribuição mundial e relatam a detecção dos coronavírus em 1 a 10% dos pacientes com infecção do trato respiratório2. Estudos recentes têm evidenciado a relação dos CoVh em casos de co-infecção com outros vírus respiratórios, como bocavírus, influenza, vírus respiratório sincicial humano e metapneumovírus humano; tais estudos foram conduzidos em países como Itália, Alemanha, Bélgica, Canadá, Estados Unidos, França, Japão, China e Tailândia1,5,6.
Não há uma relação confirmada entre a incidência do vírus a fatores climáticos, consequentemente não há uma sazonalidade bem definida para as infecções por CoVh3,6,7. Entretanto, alguns estudos têm mostrado uma maior frequência da infecção pelo vírus entre os meses de dezembro e abril8. Não existem, também, estudos que comprovem a discrepância de susceptibilidade à infecção entre faixas etárias. Estudos relativos ao CoVh são escassos no Brasil e inexistentes na Região Norte do País2,3,6. Por serem patógenos de rápida evolução e que eficientemente transpõem a barreira entre espécies, é recomendável o monitoramento de sua circulação na população humana2,5.
MATERIAIS E MÉTODOS
ASPECTOS ÉTICOS
O presente estudo foi aprovado pelo Comitê de Ética em Pesquisa do Instituto Evandro Chagas (IEC), em 22 de setembro de 2011, sob o parecer no 0027/2011.
DESENHO DO ESTUDO
O estudo foi caracterizado como transversal, observacional, sendo utilizadas amostras coletadas entre 2009 e 2011.
POPULAÇÃO DE ESTUDO
]]> Os espécimes clínicos (swab oral/nasal e aspirado nasofaríngeo) utilizados nesta investigação foram obtidos no período de agosto de 2009 a março de 2011. Os pacientes envolvidos nesta pesquisa apresentavam sinais ou sintomas sugestivos de IRA, e eram negativos para a detecção de outros vírus respiratórios como o influenzae. As amostras clínicas foram estocadas a -70o C até seu processamento laboratorial.DETECÇÃO E ANÁLISE FILOGENÉTICA DO CoVh
Extração do RNA viral (RNAv)
O RNAv foi extraído a partir do espécime clínico, utilizando-se kit comercial PureLink® Viral RNA/DNA Mini Kit (Invitrogen by Life Technologies, EUA), seguindo as orientações do fabricante. Depois de extraído o RNA foi estocado a -70o C ou imediatamente submetido a RT-PCR3,4.
Reação em cadeia mediada pela polimerase precedida de transcrição reversa (RT-PCR)
A detecção dos CoVh foi realizada por meio da técnica de RT-PCR. O procedimento foi conduzido com emprego do kit comercial Superscript® (Invitrogen by Life Technologies, EUA). As reações de RT-PCR foram realizadas em um volume final de 25 µl contendo 5,0 µl de RNA viral, 6,0 µl de H2O livre de DNAse e RNAse, 12,5 µl de PCR Master Mix (2x), 0,5 µl de Forward Primer 50 µM, 0,5 µl de Reverse Primer 50 µM, e 0,5 µL de Super Script IIITM One-Step RT-PCR System with Platinum Taq. Na amplificação a mistura foi submetida a 48o C por 30 min, 95o C por 10 min, seguida por 45 ciclos de PCR cada um composto de 95o C por 15 s e 60o C por 1 min. Todas as etapas da reação foram realizadas na plataforma Applied Biosystems7500 Real-Time PCR. Cada conjunto de amostras submetido à amplificação foi acompanhado de um controle negativo, o qual continha todos os reagentes da mistura e água livre de DNAse e RNAse, e um controle positivo para cada um dos vírus3,4.
Eletroforese em gel de agarose
Ao término da amplificação, as amostras foram analisadas por eletroforese em gel de agarose a 2%, corado por SYBR® Safe DNA Gel Stain (Invitrogen by Life Technologies, EUA), com tampão TAE 1X (tris-acetato-EDTA). O marcador de peso molecular SmartLadder® (Eurogentec, EUA) foi aplicado em cada gel. A visualização dos amplicons impregnados pelo SYBR® Safe foi realizada em transiluminador com luz ultravioleta (UV) e fotografado com auxílio do sistema de foto-documentação Vilber Loumart3,4,5.
RT-PCR para a caracterização molecular do CoVh
Visando a caracterização genética dos CoVh detectados, foi realizada a amplificação de um segmento gênico codificador da polimerase viral por meio de RT-PCR utilizando-se SuperScript IIITM One-step RT-PCR System with Platinum Taq® e oligonucleotídeos iniciadores específicos para os CoVh 229E, HKU1, NL63 e OC439,10. Cada conjunto de amostras submetido à amplificação foi acompanhado de um controle negativo (H2O livre de DNAse e RNAse) e um positivo (amostra positiva para CoVh), utilizados como padrão no teste. O produto da RT-PCR possui o tamanho, em pares de base de DNA, conforme mostrado na tabela 1.
]]>

Purificação e quantificação do produto da RT-PCR
Nas amostras que apresentaram a banda de interesse, foi realizada a purificação do produto da PCR, utilizando o kit comercial QIAquick PCR Purification (Qiagen, Alemanha), seguindo as instruções do fabricante. O produto purificado foi quantificado seguindo instruções do fabricante do marcador de peso molecular Low Mass Ladder (Invitrogen by Life Technologies, EUA)10. A concentração de cada amostra foi determinada comparando-se a intensidade das bandas do marcador com a banda das amostras, sendo o resultado expresso em nanogramas (ng).
Reação de sequenciamento
Para a reação de sequenciamento foi utilizado o Kit Big Dye® Terminator v3.1 Cycle Sequencing (Applied Biosystem, EUA) seguindo as orientações do fabricante. Em seguida as amostras foram submetidas à precipitação utilizando isopropanol e etanol. A eletroforese foi feita em sequenciador automático ABI Prism 3130x1 (Applied Biosystem), baseada no método de terminação em cadeia9.
Edição e alinhamento das sequências
As sequências nucleotídicas obtidas foram analisadas e editadas utilizando-se o programa GENEIOUS 4.8.5, e alinhadas com sequências de outros vírus isolados e disponíveis no banco de dados do GenBank (http://www. ncbi.nlm.nih.gov), utilizando o programa MAFFT v.711.
]]> Construção da árvore filogenética e análise das sequênciasAs árvores filogenéticas, bem como a matriz de distância foram construídas utilizando o programa PAUP 4.0 beta. O método usado para construção das árvores foi o de máxima parcimônia, que busca a árvore mais parcimoniosa para explicar a evolução. A análise de bootstrap usando 1.000 réplicas foi utilizada para gerar maior confidência aos valores dos grupamentos, sendo repetido o processo por dez vezes11.
RESULTADOS
No período estudado, foi detectada uma amostra positiva para o CoVh-OC43 entre 308 pacientes com IRA investigados. O paciente em questão pertencia ao sexo feminino, com 93 anos de idade e quadro clínico sugestivo de IRA.
ANÁLISE FILOGENÉTICA DO CoVh
A análise filogenética permitiu classificar a amostra positiva para o CoVh como pertencente ao subtipo OC43 do vírus como mostra a figura 1.
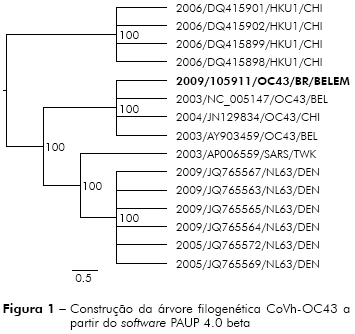
As sequências foram alinhadas com o software MAFFT, que realiza um rápido alinhamento múltiplo baseado na transformada rápida de Fourier, utilizando 1.000 repetições. A análise de saturação demonstrou que o conjunto de dados apresentava saturação para as transições, mas não para as transversões. Para a reconstrução filogenética foi escolhido o método evolutivo de máxima-parcimônia com 1.000 réplicas, utilizando-se o software PAUP 4.0, repetindo-se dez vezes o processo de análise. A sequência em questão agrupou em 100% das vezes no clado pertencente às cepas do CoVh-OC43.
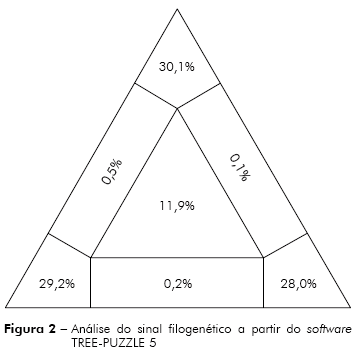
A análise de sinal filogenético, realizada com o software TREE-PUZZLE 57,9,10 demonstrou que apenas 11,9% dos táxons não tiveram suas topologias agrupadas, demonstrando que este conjunto de dados apresenta forte sinal filogenético como mostrado na figura 2.
DISCUSSÃO
O presente estudo apontou uma baixa incidência do vírus no período estudado, já que entre as 308 amostras de pacientes com quadro clínico sugestivo de IRA investigadas, foi detectada apenas uma infecção (0,33%) pela cepa OC43 do CoVh. Estes dados entram em conformidade com outros estudos conduzidos em países como: Itália, Alemanha, Bélgica, Canadá, Estados Unidos, França, Japão, China, que apontam frequência das infecções pelos distintos CoVh e evidenciam também sua baixa incidência1,2,6.
A confirmação desta infecção por CoVh corrobora com outros dados gerados por diferentes grupos de pesquisa mundiais, revelando assim que os CoVh podem estar rotineiramente associados a casos de IRA, uma vez que as diferentes cepas deste vírus têm sido apontadas como agentes emergentes associados a quadros clínicos sugestivos da doença em questão3,6.
]]> Por meio de métodos de sequenciamento de DNA descritos e já consagrados pela literatura, foi possível associar a amostra positiva encontrada à cepa OC43 dos CoVh, como ficou explícito na árvore filogenética, mostrando que não há nenhuma alteração genética que confira ao patógeno alguma virulência maior do que as já apontadas por outros estudos. O segmento gênico (codificador da enzima polimerase) sequenciado não apresentou alterações nucleotídicas significativas quando comparado a outras sequências disponíveis no Genbank evidenciando uma conservação na estrutura do seu DNA.De acordo com a Organização Mundial da Saúde, as doenças infecciosas, incluindo as IRA, são listadas entre as maiores causas de morbidade e mortalidade no mundo inteiro até o ano de 2011; os CoVh, como um dos patógenos causadores desta doença, vêm sendo inseridos nestas estatísticas, já que os distintos subtipos deste vírus (dentre eles o OC43) vêm sendo associados, a cada ano, a casos desta doença, o que os tem tornado um agente infeccioso com importância clínica mundial2,6.
CONCLUSÃO
A partir deste estudo, foi possível confirmar a circulação do CoVh em Belém, Estado do Pará no período estudado, sendo este o primeiro trabalho do gênero conduzido na Região Norte do Brasil. Apesar da baixa incidência deste vírus, seu caráter de virulência não permite desconsiderar sua alta capacidade patogênica, já que tem sido relacionado como um dos patógenos associados a IRA e suas complicações clínicas.
Portanto, recomenda-se o monitoramento de sua circulação entre a população da região para que sejam gerados dados epidemiológicos, bem como sobre a existência de um perfil de sazonalidade, e criadas alternativas profiláticas com o objetivo de diminuir os riscos de infecção por CoVh.
REFERÊNCIAS
1 Nakajima N, Hata S, Sato Y, Tobiume M, Katano H, Kaneko K, et al. The first autopsy case of pandemic influenza (A/H1N1pdm) virus infection in a Japan: detection of a high copy number of the virus in type II alveolar epithelial cells by pathological and virological examination. Jpn J Infect Dis. 2009 Jan;63(1):67-71. [Link]
2 Ksiazek TG, Erdman D, Goldsmith CS, Zaki SR, Peret T, Emery S, et al. A novel coronavirus associated with severe acute respiratory syndrome. N Engl J Med. 2003 May;348(20):1953-66. Doi: 10.1056/NEJMoa030781 [Link]
3 Van der Hoek L, Pyrc K, Jebbink MF, Vermeulen-Oost W, Berkhout RJM, Wolthers KC, et al. Identification of a new coronavirus. Nat Med. 2004 Apr;10(4):368-73. Doi: 10.1038/nm1024 [Link]
4 Woo PCY, Lau SKP, Chu CM, Chan KH, Tsoi HW, Huang Y, et al. Characterization and complete genome complete sequence of a novel coronavirus, coronavirus HKU1 from patients with pneumonia. J Virol. 2005 Jan;79(2):884-95. Doi: 10.1128/JVI.79.2.884-895.2005 [Link]
5 Yamada Y, Liu XB, Fang SG, Tay FPL, Liu DX. Acquisition of cell-cell fusion activity by amino acid substitutions in spike protein determines the infectivity of coronavirus in cultured cells. PLoS ONE. 2009 Jul;4(7):e6130. Doi:10.1371/journal.pone.0006130 [Link]
6 Shek LPC, Lee BW. Epidemiology and seasonality of respiratory tract virus infections in the tropics. Paediatr Respir Rev. 2003 Jun;4(2):105-11. Doi: 10.1016/S1526-0542(03)00024-1 [Link]
7 Nelson MI, Simonsen L, Viboud C, Miller MA, Holmes EC. Phylogenetics analysis reveals the global migration of seasonal influenza A viruses. PloS Pathog. 2007 Sep;3(9):e131. Doi:10.1371/journal.ppat.0030131 [Link]
8 Gaunt ER, Hardie A, Claas ECJ, Simmonds P, Templeton KE. Epidemiology and clinical presentations of the four human coronaviruses 229E, HKU1, NL63, and OC43 detected over 3 years using a novel multiplex real-time PCR method. J Clin Microbiol. 2010 Aug;48(8):2940-7. Doi: 10.1128/JCM.00636-10 [Link]
9 Sanger F, Nicklen S, Coulson AR. DNA sequencing with chain-terminating inhibitors. Proc Natl Acad Sci USA. 1977 Dec;74(12):5463-7. [Link]
10 Kumar S, Tamura K, Jakobsen I, Nei M. MEGA2: molecular evolutionary genetics analysis software. Bioinformatics. 2001 Dec;17(12):1244-5. Doi: 10.1093/bioinformatics/bts507 [Link]
11 Felsenstein J. Confidence-limits on phylogenies: an approach using the bootstrap. Evolution. 1985;39:783-91. Doi: 10.2307/2408678 [Link]
]]>
 Correspondência / Correspondence / Correspondencia:
Correspondência / Correspondence / Correspondencia:
Wyller Alencar de Mello
Seção de Virologia,
Instituto Evandro Chagas/SVS/MS
Rodovia BR 316, km 7, s/no.
Bairro: Levilândia CEP: 67030-000
Ananindeua-Pará-Brasil
Tel.: (91) 3214-2005 / 3214-2013
Recebido em / Received / Recibido en: 10/2/2014 ]]> Aceito em / Accepted / Aceito en: 4/4/2014
]]>